
2019年8月26日
感染制御プロジェクト 真田崇弘研究員らは「全ゲノムシークエンスおよびRNAシークエンスを基盤としたツパイゲノムデータベースの構築」について英国科学雑誌「Scientific Reports」に発表しました。
全ゲノムシークエンスおよびRNAシークエンスを基盤としたツパイゲノムデータベースの構築
- <論文名>
- ”Construction of complete Tupaia belangeri transcriptome database by whole-genome and comprehensive RNA sequencing”
- <発表雑誌>
- 英国科学雑誌「Scientific Reports」
DOI : https://doi.org/10.1038/s41598-019-48867-x
URL:https://www.nature.com/articles/s41598-019-48867-x
研究の背景
ツパイはリスのような外見をもつ小型の哺乳動物で、遺伝学的にヒトに近縁な動物です。ツパイはこれまでB型肝炎ウイルスやC型肝炎ウイルスに感染感受性を示すことから、これらの感染モデル動物として使われてきましたが、近年、インフルエンザなど他の感染症やうつ病、視覚に関する研究に応用されるなどその使用は多分野に渡っています。
このようにツパイは実験動物として高い有用性を持つ一方で、より詳細な解析を進めるうえで必須となる遺伝子情報が十分とはいえず、ツパイの遺伝子の解析・同定が求められていました。
研究の概要
我々は、ツパイの全ゲノムシークエンスおよびRNAシークエンスを行い、これらのデータを統合して、ツパイの遺伝子情報の網羅的な解析を行いました。さらに、ツパイの各遺伝子の蛋白質翻訳領域の塩基配列を同定すべく、遺伝子情報を選別し、12,612遺伝子の蛋白質翻訳領域の塩基配列を同定しました。さらに、本研究により得られたデータをより多くの研究者に利用していただくために、無料のツパイのゲノムデータベースサイトを構築しました(TupaiaBase : http://tupaiabase.org  )。
)。
また今回同定した12,612遺伝子をもとに、B型肝炎ウイルス感染ツパイ個体での感染初期における遺伝子変動を網羅的に解析しました。その結果、肝臓において感染後1日目よりⅠ型インターフェロン応答に関わる遺伝子が抑制されていることが明らかとなりました。
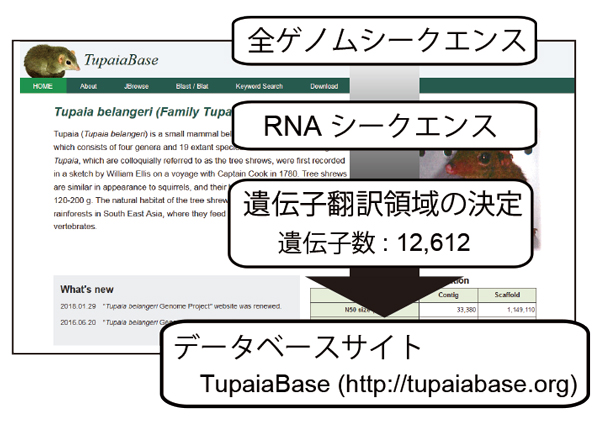
TupaiaBase : http://tupaiabase.org 
今後の展望
本研究により、ツパイの膨大な遺伝子情報が得られ、それらを基に信頼性の高いツパイのゲノムデータベースサイトを構築できました。これらの遺伝子情報およびデータベースサイトの利用を通して、ツパイのモデル動物としての有用性が高まるとともに、世界中で広く行われているツパイを用いた様々な研究に寄与することが期待されます。


